© Yimin Zheng
News • Open-Source-KI-Software
Digitale Pathologie: Vom Gewebeschnitt zur Datenquelle
Mikroskopische Bilder menschlicher Gewebe sind ein Grundpfeiler der biomedizinischen Forschung und der klinischen Diagnostik. Trotz ihrer zentralen Bedeutung lassen sich diese Bilder jedoch häufig nur schwer systematisch auswerten und mit anderen biologischen Datentypen verknüpfen.
Eine neue Studie unter der Leitung von CeMM Principal Investigator André Rendeiro, veröffentlicht in Nature Methods, stellt mit „LazySlide“ ein Open-Source-Softwaretool vor, das die Möglichkeiten von KI, die mit großen Daten trainiert wird (sog. „Foundation Models“) nutzt und die Analyse digitaler Pathologie demokratisieren soll.
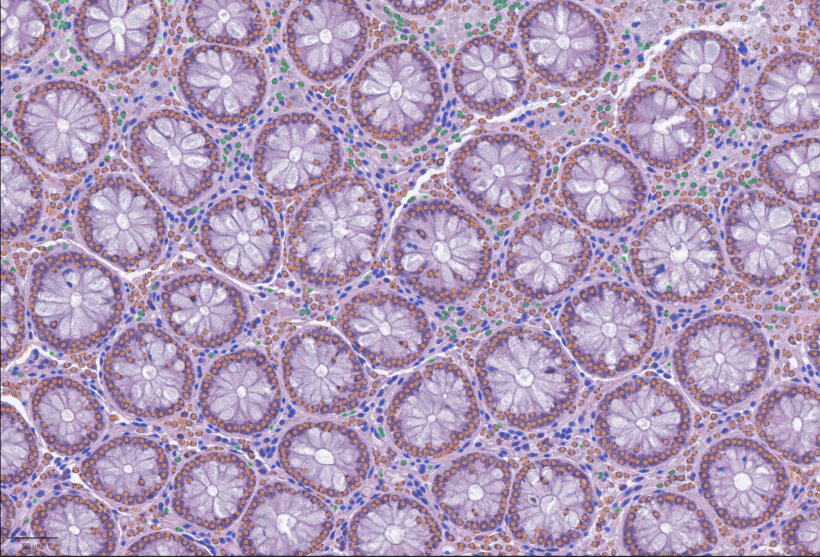
Eine entzündete Arterie, ein Tumor, der in die Lunge einwächst, oder feine Schäden in einem Organ – wenn Ärzte oder Forschende verstehen wollen, was im Inneren eines Gewebes geschieht, gehört das Mikroskop nach wie vor zu den verlässlichsten Werkzeugen. Heute sind diese Untersuchungen weitgehend digitalisiert: Eine einzelne Gewebeprobe kann als sogenanntes „Whole-Slide-Bild“ gescannt werden, das so detailreich ist, dass man von einer Übersicht des gesamten Gewebes bis hinunter zu einzelnen Zellen zoomen kann.
Indem wir Gewebebilder als reichhaltige Datensätze und nicht als statische Abbildungen behandeln, können wir neue Einblicke gewinnen, wie Krankheiten die menschliche Biologie prägen
André Rendeiro
Diese riesigen Bilder enthalten enorme Informationsmengen über Gewebe auf unterschiedlichen Skalen, sind jedoch auch sehr komplex und oft schwer mit modernen, datengetriebenen Methoden zu analysieren. Während sich in der Genetik und der Einzelzellbiologie effektive Standards für den Austausch und den Vergleich von Daten etabliert haben, lassen sich digitale Pathologiebilder nur schwer integrieren – sie liegen häufig in Softwarespezifischen Formaten vor, werden mit inkompatiblen Werkzeugen verarbeitet und sind schwer mit molekularen Informationen wie RNA-Sequenzierungsdaten zu verknüpfen. Dadurch bleiben digitalisierte Gewebebilder in vielen Forschungs- und klinischen Bereichen weitgehend ungenutzt.
Eine neue Studie aus der Forschungsgruppe von CeMM Principal Investigator André Rendeiro stellt nun LazySlide vor, eine Open-Source-Anwendung, die die Analyse von Whole-Slide-Bildern zugänglicher, kompatibler und besser in jene rechnergestützten Workflows integrierbar machen soll, die bereits die moderne Genomik prägen.
LazySlide ermöglicht es Wissenschaftlern, Whole-Slide-Bilder in kleinere, handhabbare Bereiche zu unterteilen und diese mit fortgeschrittenen KI-Modellen zu analysieren. Diese Modelle erkennen Muster in der Gewebestruktur, identifizieren unterschiedliche Zelltypen und quantifizieren feine Veränderungen der Gewebearchitektur – ohne dass aufwendige manuelle Anmerkungen erforderlich sind.

© Wolfgang Däuble / CeMM
Allem voran zeigt die Studie, wie sich visuelle Informationen aus Gewebebildern direkt mit molekularen Daten wie Genexpressionsprofilen verknüpfen lassen. In einem Beispiel analysierten die Forschenden Arteriengewebe mit und ohne Verkalkung, einem pathologischen Prozess, der mit Herz-Kreislauf-Erkrankungen assoziiert ist. LazySlide unterschied nicht nur gesundes von erkranktem Gewebe allein anhand der Bildmerkmale, sondern machte auch biologische Signalwege wie entzündliche Signalprozesse sichtbar, die erst durch die gemeinsame Analyse von Bilddaten und RNA-Sequenzierungsdaten erkennbar wurden.
„Die Histologie enthält eine enorme Menge biologischer Information, ist aber oft nur schwer zugänglich für computerunterstützte Verfahren“, sagt Yimin Zheng, Erstautor der Studie. „Mit LazySlide wollten wir ein Werkzeug bereitstellen, das es Forschenden erlaubt, Gewebebilder systematisch und quantitativ zu untersuchen und das, was sie unter dem Mikroskop sehen, mit den zugrunde liegenden molekularen Prozessen zu verbinden.“
Eine für die Forschenden besonders praktische Funktion von LazySlide ist die Möglichkeit, Bilder mit natürlicher Sprache zu verknüpfen. Mithilfe von KI-Modellen, die visuelle Muster mit textlichen Konzepten verbinden, können sie Fragen stellen wie etwa, wo in einer Gewebeprobe Anzeichen von „Verkalkung“ auftreten. Die Software hebt entsprechende Regionen hervor und erzeugt quantitative Scores, wodurch visuelle Eindrücke in messbare Daten überführt werden. Dieser Ansatz ermöglicht auch sogenannte „Zero-Shot“-Analysen: LazySlide kann das Ursprungsorgan von Gewebeproben erkennen oder gesundes von krankem Gewebe unterscheiden, ohne für jede einzelne Fragestellung spezifisch trainiert worden zu sein. Dadurch sinkt die Hürde für den Einsatz fortgeschrittener Bildanalysemethoden in der biomedizinischen Forschung erheblich.
LazySlide wurde so konzipiert, dass es sich nahtlos in bestehende rechnergestützte Werkzeuge der Biologie integriert, die in der Genomik und Einzelzellforschung weit verbreitet sind. Indem digitale Pathologie besser mit diesen etablierten Workflows verzahnt wird, trägt die Software dazu bei, Gewebebildgebung stärker in das Ökosystem datengetriebener Lebenswissenschaften einzubinden.
„Unser Ziel war es, die Analyse von Whole-Slide-Bildern zugänglicher zu machen und besser mit den Datentypen zu verknüpfen, die Forschende im Alltag nutzen“, sagt André Rendeiro. „Indem wir Gewebebilder als reichhaltige Datensätze und nicht als statische Abbildungen behandeln, können wir neue Einblicke gewinnen, wie Krankheiten die menschliche Biologie prägen.“
Die in Nature Methods veröffentlichte Studie zeigt, dass Open-Source-Werkzeuge wie LazySlide die Forschung beschleunigen und helfen können, die Lücke zwischen Gewebestruktur und molekularer Funktion zu schließen – ein wesentlicher Beitrag zu einem ganzheitlichem Verständnis von Gesundheit und Krankheit.
Quelle: CeMM Forschungszentrum für Molekulare Medizin der Österreichischen Akademie der Wissenschaften
25.03.2026





