© Helmholtz Zentrum München
News • Zelldynamik-Software "scVelo"
KI & Einzelzellgenomik sagen das "Schicksal" einer Zelle voraus
Die Erforschung der Zelldynamik ermöglicht einen tieferen Einblick in die Entstehung und Entwicklung von Zellen sowie ein besseres Verständnis von Krankheitsverläufen.
Wissenschaftler des Helmholtz Zentrums München und der Technischen Universität München (TUM) haben „scVelo“ entwickelt – eine auf maschinellem Lernen basierende Methode und Open-Source-Software, welche die Dynamik der Genaktivität in einzelnen Zellen prognostizieren kann. Damit können die Forscher den künftigen Zustand einzelner Zellen vorhersagen.
Ihre Erkenntnisse veröffentlichten die WIssenschaftler nun im Journal Nature Biotechnology. Die Software steht unter http://www.scvelo.org/ zum Download bereit.
Wir haben dynamische Prozesse bei der Lungenregeneration untersucht – und das ist erst der Anfang“, sagt
Volker Bergen
Herkömmliche Verfahren für die Einzelzellsequenzierung erlauben es, Erkenntnisse über Unterschiede und Funktionen auf zellulärer Ebene zu gewinnen – allerdings nur als statische Momentaufnahme und nicht als Zeitraffer. Diese Einschränkung macht es schwierig, Rückschlüsse auf die Zelldynamik zu ziehen. Mit der kürzlich eingeführten Methode „RNA Velocity" kann der Entwicklungsverlauf einer einzelnen Zelle rechnerisch rekonstruiert werden (auf Grundlage des Verhältnisses von gespleißten und ungespleißten Transkripten). Diese Methode war allerdings bislang nur auf statische Zellpopulationen anwendbar. Die Forscher suchten daher nach Möglichkeiten, das Konzept von „RNA Velocity" methodisch zu erweitern, sodass es auch auf dynamische Populationen anwendbar ist. Solche Zellpopulationen sind für das Verständnis von Zellentwicklung und Reaktionen auf Krankheiten von entscheidender Bedeutung.
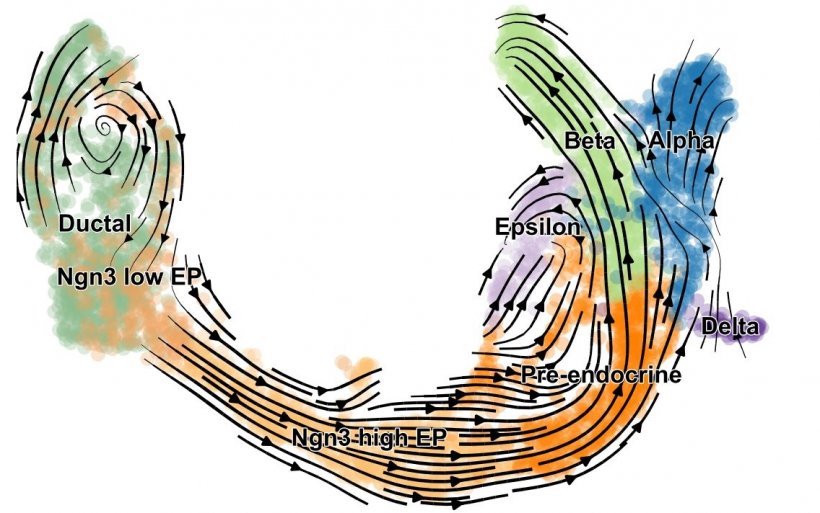
Ein Team des Instituts für Computational Biology am Helmholtz Zentrum München und der Fakultät für Mathematik der TUM entwickelten „scVelo“ (Single-cell Velocity). Die Methode ermittelt die RNA-Geschwindigkeit mit einem Modell basierend auf künstlicher Intelligenz (KI). Dabei lernt die KI die gesamte Transkriptionsdynamik für jedes Gen. Dies ermöglicht es den Forschern, das Konzept von RNA Velocity auf eine Vielzahl biologischer Systeme einschließlich dynamischer Populationen zu übertragen. „Wir haben scVelo genutzt, um die Zellentwicklungen in der endokrinen Bauchspeicheldrüse und im Hippocampus zu entschlüsseln. Außerdem haben wir dynamische Prozesse bei der Lungenregeneration untersucht – und das ist erst der Anfang“, sagt Volker Bergen, Entwickler von scVelo und Erstautor der Veröffentlichung.
Mit scVelo können die Forscher ohne aufwändige Experimente Reaktionsraten ermitteln und damit herausfinden, in welcher Geschwindigkeit die RNA produziert und gespleißt wird, und wie schnell sie schließlich zerfällt. Diese Raten können helfen, die Zellidentität und phänotypische Unterschiede besser zu verstehen. Durch die Einführung einer sogenannten Latenzzeit können sie die Zellentwicklung vollständig rekonstruieren und jede Zelle entlang ihres Entwicklungsverlaufs positionieren. Dadurch werden insbesondere die Entscheidungsprozesse einer Zelle besser verständlich. Darüber hinaus deckt scVelo regulatorische Veränderungen auf und identifiziert die Gene, welche für diese Veränderungen jeweils verantwortlich sein könnten. So können die Forscher nicht nur verstehen wie, sondern auch warum sich Zellen auf diese oder jene Weise entwickeln.
KI-basierte Lösungen wie scVelo könnten bei der Entwicklung von personalisierten Behandlungsmethoden helfen. Der Sprung von statischen Momentaufnahmen zu volldynamischen Systemen erlaubt es den Forschern, von rein deskriptiven zu prädiktiven Modellen überzugehen. In Zukunft könnten so Krankheitsverläufe, beispielsweise die Tumorbildung, besser verstanden oder auch die Zellantwort als Reaktion auf eine Krebsbehandlung entschlüsselt werden. „scVelo wurde seit der Veröffentlichung im letzten Jahr knapp 60.000 Mal heruntergeladen. Die Software ist zu einem populären und wichtigen Werkzeug für die Entwicklung kinetischer Modelle für die Einzelzell-Transkriptomik geworden“, ergänzt Prof. Fabian Theis, der die Studie konzipierte und als Direktor am Institut of Computational Biology am Helmholtz Zentrum München und als Lehrstuhlinhaber für Mathematische Modellierung biologischer Systeme an der TUM tätig ist.
Quelle: Helmholtz Zentrum München
04.08.2020





