Foto: Christian Jogler
News • Hilfe aus der Tiefe
Antibiotika aus dem Meer
Dem Team um Prof. Dr. Christian Jogler von der Friedrich-Schiller-Universität Jena ist es gelungen, mehrere Dutzend bisher wenig beachtete Bakterien aus dem Meer im Labor zu kultivieren, funktionell zu charakterisieren und so einem systematischen Wirkstoff-Screening zugänglich zu machen.
Erste bioinformatische Analysen und zellbiologische Beobachtungen deuten auf ein Potenzial zur Produktion neuer Antibiotika hin. Darüber berichten die Forscher in der aktuellen Ausgabe der Fachzeitschrift Nature Microbiology.

Fast drei Viertel aller klinisch relevanten Antibiotika sind Naturstoffe – produziert von Bakterien. Doch die heute verfügbaren Antibiotika verlieren ihre Wirksamkeit, immer mehr Krankheitserreger sind gegen sie resistent. Neue Antibiotika werden also dringend gebraucht. Allerdings stehen für die Wirkstoffsuche derzeit weniger als ein Prozent der bekannten Bakterienarten zur Verfügung, die übrigen 99 Prozent gelten als „unkultivierbar“ und sind daher kaum erforscht.
Die Fähigkeit Antibiotika zu produzieren, ist unter Bakterien zudem nicht gleichmäßig verteilt. „Sie ist vor allem in Mikroorganismen mit komplexen Lebensweisen zu finden, einer ungewöhnlichen Zellbiologie und großen Genomen“, erklärt Prof. Dr. Christian Jogler von der Friedrich-Schiller-Universität Jena. „Solche Organismen produzieren antibiotische Verbindungen und setzen sie im Kampf um Nährstoffe und Lebensräume gegen andere Bakterien ein“, so der Mikrobiologe weiter. Wo immer solche mikrobiologischen Verteilungskämpfe auftreten und Nährstoffe knapp sind, sei ein aussichtsreicher Ort, um nach potenziellen Antibiotikaproduzenten zu suchen.
Die Ergebnisse dieser Analysen belegen, dass die neu gewonnenen Planctomyceten außergewöhnlich komplexe Lebensweisen besitzen und über das Potenzial verfügen, neue Antibiotika produzieren zu können
Sandra Wiegand
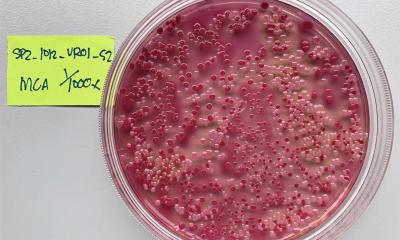
Genau das haben Prof. Jogler und sein Team getan: Mit Tauchrobotern und wissenschaftlichen Tauchern haben sie an insgesamt zehn Orten im Meer nach sogenannten Planctomyceten gesucht. „Wir wissen, dass Planctomyceten in Gemeinschaften mit anderen Mikroorganismen leben, und mit diesen um Lebensraum und Nährstoffe konkurrieren“, erklärt Jogler den Grund, der diese Gruppe von Bakterien für die Forscher interessant macht. Aus den Proben aus dem Mittelmeer, der Nord- und Ostsee, dem Schwarzen Meer sowie dem Atlantik, dem Pazifik und dem Nordpolarmeer gelang es den Wissenschaftlerinnen und Wissenschaftlern insgesamt 79 neue Planctomyceten in Reinkultur zu bringen. „Zusammen bilden diese Reinkulturen 31 neue Gattungen und 65 neue Arten“, ergänzt Dr. Sandra Wiegand, die Erstautorin der Studie.
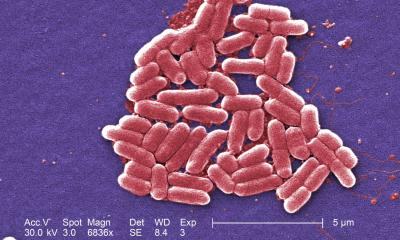
Um die neu gewonnenen Reinkulturen zu charakterisieren kamen bioinformatische und mikroskopische Methoden zum Einsatz. „Die bioinformatische Analyse war dabei ganzheitlich angelegt“, sagt Dr. Wiegand. Das Potenzial kleine Moleküle wie Antibiotika zu produzieren, sei genauso untersucht worden, wie die Prozesse der zellulären Signalverarbeitung. Diese sind ein Maß für die Komplexität der mikrobiellen Lebensweise und damit ein weiterer Hinweis auf eine Antibiotikaproduktion. „Die Ergebnisse dieser Analysen belegen, dass die neu gewonnenen Planctomyceten außergewöhnlich komplexe Lebensweisen besitzen und über das Potenzial verfügen, neue Antibiotika produzieren zu können.“
Einen Teil ihrer bioinformatischen Analysen konnten die Forscherinnen und Forscher bereits in der vorliegenden Studie experimentell bestätigen. So haben sie unter anderem die Zellbiologie der isolierten Planctomyceten untersucht. „Sie teilen sich ganz anders als alle kritischen pathogenen Bakterien“, so Prof. Jogler. Die Arbeiten zeigen zudem unerwartete neue Mechanismen der bakteriellen Zellteilung. Vor allem aber belege die Studie eindrücklich, dass auch vermeintlich „unkultivierbare“ Bakterien in Reinkultur gewonnen und charakterisiert werden können.
Viele Aspekte ihrer aktuellen Arbeit, so die Autoren der Studie, werden sich auf andere potenzielle Antibiotikaproduzenten übertragen lassen. „Die Hypothesen-getriebene Kultivierung und ganzheitliche Charakterisierung ist zwingend erforderlich, um wirklich Neues zu entdecken und neue therapeutische Wege zu ermöglichen“, betont Prof. Jogler, der erst vor wenigen Wochen nach Jena gewechselt ist. Der Professor für Mikrobielle Interaktion freut sich nun an der Friedrich-Schiller-Universität mit ihrem Exzellenzcluster „Balance of the Microverse“ ein optimales Umfeld für seine Forschung gefunden zu haben.
Quelle: Friedrich-Schiller-Universität Jena
19.11.2019