© S. Homolka, Forschungszentrum Borstel, Leibniz Lungenzentrum / Finci et al., Lancet Microbe 2022 (CC BY 4.0)
News • Mutationen im Bakterien-Genom
Tuberkulose: Antibiotika-Behandlungsstrategien personalisieren
Tuberkulose zählt mit ca. 1.4 Millionen Todesfällen und zehn Millionen Erkrankten pro Jahr zu den häufigsten Todesursachen weltweit. Resistente und multiresistente (MDR) Varianten des Tuberkuloseerregers Mycobacterium tuberculosis stellen eine große Gefahr für die Kontrolle der Tuberkulose und die globale Gesundheit dar.
Mutationen im Erbgut von M. tuberculosis-Bakterien, die in Verbindung mit Antibiotikaresistenzen stehen, kommen bei MDR-Tuberkulose Patienten in unterschiedlichen Kombinationen vor. Um Erkrankte zielgerichtet behandeln und die Übertragung von Antibiotika-resistenten Tuberkulosebakterien erfolgreich eindämmen zu können, ist die rasche Erkennung dieser patientenspezifischen Resistenzmuster daher von entscheidender Bedeutung. Mit einer in der Fachzeitschrift Lancet Microbe veröffentlichten internationalen Studie sind Forschende des Deutschen Zentrums für Infektionsforschung (DZIF) diesem Ziel nun einen großen Schritt nähergekommen.
Unsere Studie zeigt auch, dass die Erbgutanalyse der Bakterien bereits eine präzise Vorhersage von Resistenzen gegen wichtige Tuberkulose-Antibiotika ermöglicht und viele der klassischen und oft langwierigen Tests ersetzen kann
Stefan Niemann
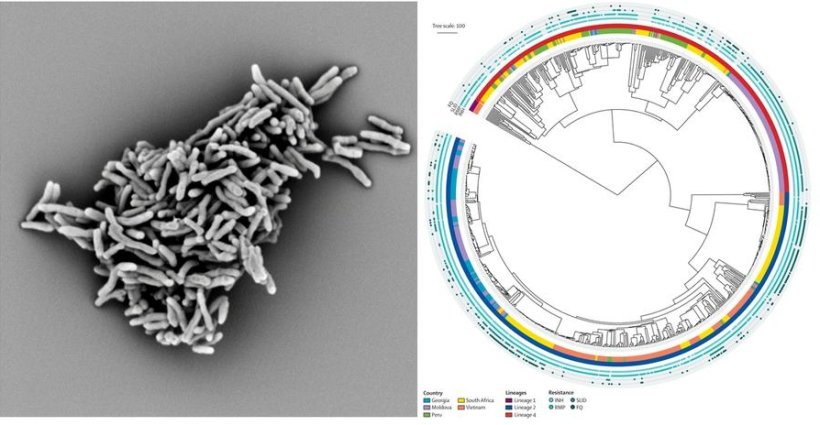
In der multizentrischen Beobachtungsstudie sequenzierten DZIF-Wissenschaftler des Forschungszentrums Borstel und des Universitätsklinikums Heidelberg die Genome einer großen Anzahl klinischer M. tuberculosis-Isolate aus der ganzen Welt. Dabei fanden die Forschenden, dass bestimmte Veränderungen (Mutationen) im Bakterien-Genom mit der Wirksamkeit von Antibiotika bei den betreffenden Tuberkulose-Erkrankten eng korrelierten. Die Identifizierung bestimmter Mutationen im Bakterien-Genom ermöglicht daher potentiell eine Vorhersage darüber, welche Antibiotika bei einem Patienten noch wirken, beziehungsweise, ob die Dosis erhöht werden sollte. Mit diesem Wissen lässt sich der Erfolg der initialen Antibiotikatherapie steigern und die weitere Übertragung des Erregers verhindern. “Die Sequenz-Analyse ermöglicht uns ein besseres Verständnis der genetischen Grundlagen für Resistenzen gegen Tuberkulosemedikamente und deshalb eine schnellere, personalisierte Tuberkulose-Behandlung,“ resümiert PD Dr. Claudia Denkinger, Letztautorin der Publikation.
„Wir haben in der vergleichenden Genomanalyse zum Beispiel auch Veränderungen im Erbgut der Bakterien beobachtet, die nicht immer zu eindeutigen Ergebnissen bei der klassischen – auf Bakterienkulturen-basierenden – Resistenztestung führen, aber möglicherweise die Therapie beeinflussen können“, sagt Dr. Matthias Merker, einer der Erstautoren der Studie und Schleswig-Holstein Excellence-Chair Nachwuchsgruppenleiter am Forschungszentrum Borstel.
„Unsere Studie zeigt auch, dass die Erbgutanalyse der Bakterien bereits eine präzise Vorhersage von Resistenzen gegen wichtige Tuberkulose-Antibiotika ermöglicht und viele der klassischen und oft langwierigen Tests ersetzen kann“, fügt Prof. Stefan Niemann vom Nationalen Referenzzentrum für Mykobakterien in Borstel, einer der Letztautoren der Studie, an. „In Zukunft wollen wir diese bakterielle Genomanalysetechnik speziell in den Tuberkulose-Schwerpunkten im südlichen Afrika, Osteuropa und Zentralasien weiter ausbauen.“
Quelle: Deutsches Zentrum für Infektionsforschung
02.09.2022